- 1零基础学鸿蒙,从入门到实践鸿蒙开发学习攻略_鸿蒙教程
- 2掌握ChatGPT:提示工程入门详解
- 3bert模型取last_hidden_state[:, 0]_bert输出lasthidd
- 4Eureka的理解和使用
- 5Kafka入门,这一篇就够了(安装,topic,生产者,消费者)_kafka消费者组topic和sink(2)_kafka topic 消费组
- 6Ubuntu交叉编译libusb库_libusb ubuntu编译
- 7计算机专业英语词汇
- 8kafka的工作原理分析(一)_kafka工作原理
- 9Mac苹果电脑不能拷贝文件到U盘怎么办?_mac电脑复制文件到u盘闪退
- 10深入探索多头注意力机制:深度学习的关键创新_多头注意机制
利用conda进行R的安装_conda安装r
赞
踩
1.miniconda3的安装
官网:Miniconda — Conda documentation
找到对应系统、Python版本下载
- wget https://mirrors.ustc.edu.cn/anaconda/miniconda/Miniconda3-latest-Linux-x86_64.sh
- #wget -c https://repo.continuum.io/miniconda/Miniconda3-latest-Linux-x86_64.sh
-
- bash Miniconda-latest-Linux-x86_64.sh
2. 设置conda镜像源
依次输入以下命令设置软件镜像源,并展示镜像源地址,一般设下载地址为清华,也可以选择其他。注意,要用 bioconda 源,必须先设置 conda-forge 源,并且 conda-forge 源优先级是最高的
清华:anaconda | 镜像站使用帮助 | 清华大学开源软件镜像站 | Tsinghua Open Source Mirror
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/pkgs/free/
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/pkgs/main/
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/cloud/bioconda/
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/cloud/conda-forge/
- conda config --set show_channel_urls yes
北外镜像:
- conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/pkgs/free/
- conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/pkgs/main/
- conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/pkgs/r/
- conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/cloud/bioconda/
- conda config --add channels https://mirrors.bfsu.edu.cn/anaconda/cloud/conda-forge/
- conda config --set show_channel_urls yes
中科大:
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/pro
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/r
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/free
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/pkgs/main
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/bioconda
- conda config --add channels https://mirrors.ustc.edu.cn/anaconda/cloud/conda-forge
- conda config --set show_channel_urls yes
其他一些命令:
- conda config --show channels #显示镜像源
- conda config --show-sources #显示镜像源
- conda config --remove channels https://*** #删除镜像源
3. 创建流程环境
- 创建rna流程环境,指定python版本为3,同时下载sra-tools 软件
- conda create -n rna_p3 python=3 sra-tools
- conda env list #查看环境
- conda activate rna_p3 #进入conda 环境
- conda deactivate #退出当前conda环境
- 如果想重命名环境:先新建clone再进行删除
- conda create -n rna --clone rna_p3
- conda remove -n rna_p3 --all
4. 软件的下载管理
conda安装包在线查询 https://anaconda.org/
- conda install (-y)软件名 # 安装软件
- conda install 软件名=版本号 # 安装特定版本软件
- conda search 软件名 #搜索软件
- conda list # 列出已安装软件
- conda update 软件名 #更新软件
- conda remove 软件名 #卸载软件
5. 在脚本中切换conda环境
若想在脚本中切换conda环境,脚本内容如下,脚本执行完后会自动退回当前环境
- source ~/miniconda3/bin/activate rna_p3
- python --version
- conda info --envs
- #####命令
- python --version
- conda info --envs
或者先在脚本执行source ~/miniconda3/etc/profile.d/conda.sh,再使用conda命令
6. 环境迁移:导出安装包列表成为yaml文件
如果想要迁移环境中的安装包到其他计算机上,可以导出yaml文件
- conda env export --file rna_p3_env.yaml --name rna_p3
- conda env create -f rna_p3_env.yaml
2.安装R环境
1. 提前准备好conda的R单独环境
- conda env list #查看已有环境
-
- conda create -n R4.1.2
-
- conda activate R4.1.2
-
- #激活环境
- source activate R4.1.2

2. 进入环境后,多添加一些conda channel
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/pkgs/free
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/cloud/conda-forge
- conda config --add channels https://mirrors.tuna.tsinghua.edu.cn/anaconda/cloud/bioconda
- conda config --set show_channel_urls yes
- conda config --show
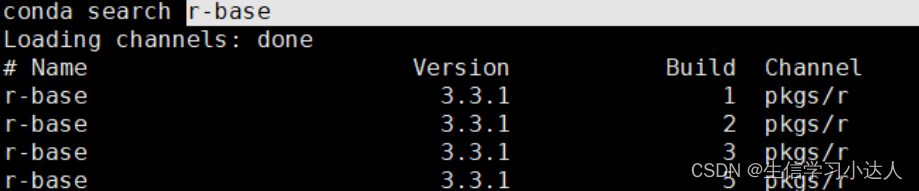
选择一款适合的版本
- conda install r-base=4.1.2
-
- which -a R
将自己刚才安装的R绝对路径添加到.bashrc中的环境变量中$PATH,也可以加alias。
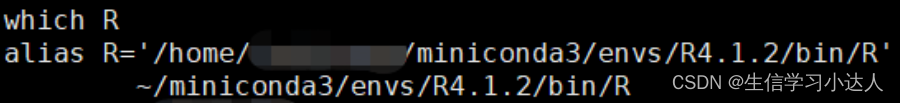
如今,R的环境已经安装好了。
3.安装R包
options()$repos #查看现有镜像file.edit(file.path("~",".Rprofile")) #打开一个文件
在文件中写入下面的内容 #多写几个镜像
options("repos"=c(CRAN="https://mirrors.pku.edu.cn/CRAN/","The Comprehensive R Archive Network","http://mirrors.aliyun.com/CRAN"))
print("已设置北大阿里云镜像")
写完后,退出()
- #退出R语言
- q()
-
- #重新进行R
- R
重新进入R
options()$repos #查看现有镜像
2. 安装BiocManager ##官网Bioconductor - Install
R4.1.2对应的BiocManager版本是3.14
在R中输入
if (!require("BiocManager",quietly = TRUE))
install.packages("BiocManager")
BiocManager::install(version ="3.14")
3. 安装R包
方法一:>install.packages("package_name")
方法二:
> library(BiocManager)
> BiocManager::install("ggplot2")
OK,此时你可以安装自己想要的R包了。
#附些常见的命令,查看已安装的R包“library()”。加载包“library(packagename)”。查看已加载的包“(.packages())”。取消已加载的包“detach("package: packagename")”。
例如安装一些常见的R包:
安装:install.packages("dplyr")
加载:library(dplyr)
查看帮助文档(函数的不同参数使用说明):?dplyr


