热门标签
热门文章
- 1VM虚拟机中的centOS7如何安装linux QQ_vmware workstation centos qq下载
- 2智能智慧型停车场管理系统解决方案_智慧停车后台管理系统,前端技术
- 3node-npm 设置淘宝镜像_node设置淘宝镜像
- 4rk3566安装Armbian实践
- 5Unity 通过代码实现Texture2D可读写_unity texture2d 读写
- 6iOS 为现有工程接入flutter-基础配置篇_flutter项目ios flutter_root
- 7不同版本CUDA和cudnn下载安装并配置环境变量_cuda下载按照
- 8tensorflow.keras.backend.mean() 与 tf.reduce_mean()_keras reduce_mean
- 9linux重置root用户密码_linux修改root密码
- 10iter() iter.next()
当前位置: article > 正文
机器学习:Kernel PCA核主成分分析
作者:很楠不爱3 | 2024-02-22 07:31:38
赞
踩
核主成分分析
1. kernel PCA 概述
核主成分分析(Kernelized PCA,KPCA)利用核技巧将d维线性不可分的输入空间映射到线性可分的高维特征空间中,然后对特征空间进行PCA降维,将维度降到d′ 维,并利用核技巧简化计算。也就是一个**先升维后降维【数据先通过核函数(kernel function)转换成一个新空间,也就是升维过程,然后再用PCA进行降维处理】**的过程,这里的维度满足d′<d<D

线性降维方法假设从高维空间到低维空间的函数映射是线性的,然而在有些时候,高维空间是线性不可分的,需要找到一个非线性函数映射才能进行恰当的降维,这就是非线性降维。
KPCA就是一种非线性降维方法
2. KPCA的实施步骤
以 Radial Basis Function(RBF) kernel PCA(不同的核,体现在代码上仅仅是一处细微的差别)为例进行说明:
- 计算核矩阵***K***【相似度矩阵】
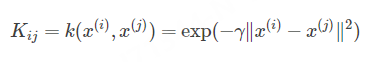
这是最为常见的RBF(Rational Basis Function)核函数,也有多项式核:
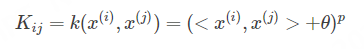
和sigmoid型(hyperbolic tangent)核:
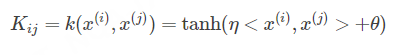
其矩阵形式也即:
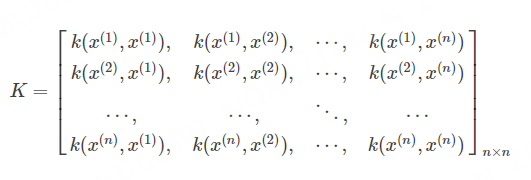
- center the K
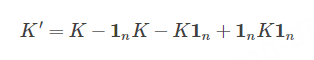
其中 1n是 n×n 的元素值全为1/n矩阵 - 对 K′进行特征值分解,获得对应于前 k个特征值的特征向量。与标准PCA算法不同的是,这里获得特征向量不再是 principal component axes,而已经是全部样本在这些轴上的投影了,也即是我们所需的进行降维后的数据了。
3. Python实现KPCA与PCA
3.1 Case1:
import numpy as np import matplotlib.pyplot as plt #构建样本数据 A1_mean = [1, 1] A1_cov = [[2, .99], [1, 1]] A1 = np.random.multivariate_normal(A1_mean, A1_cov, 50) A2_mean = [5, 5] A2_cov = [[2, .99], [1, 1]] A2 = np.random.multivariate_normal(A2_mean, A2_cov, 50) A = np.vstack((A1, A2)) B_mean = [5, 0] B_cov = [[.5, -1], [.9, -.5]] B = np.random.multivariate_normal(B_mean, B_cov, 100) f = plt.figure(figsize=(10, 10)) ax = f.add_subplot(111) ax.set_title("$A$ and $B$ processes") ax.scatter(A[:, 0], A[:, 1], color='r') ax.scatter(A2[:, 0], A2[:, 1], color='r') ax.scatter(B[:, 0], B[:, 1], color='b') #KPCA处理结果 from sklearn.decomposition import KernelPCA kpca = KernelPCA(kernel='cosine', n_components=1) AB = np.vstack((A, B)) AB_transformed = kpca.fit_transform(AB) A_color = np.array(['r']*len(B)) B_color = np.array(['b']*len(B)) colors = np.hstack((A_color, B_color)) f = plt.figure(figsize=(10, 4)) ax = f.add_subplot(111) ax.set_title("Cosine KPCA 1 Dimension") ax.scatter(AB_transformed, np.zeros_like(AB_transformed), color=colors) #PCA处理结果 from sklearn.decomposition import PCA pca = PCA(1) AB_transformed_Reg = pca.fit_transform(AB) f = plt.figure(figsize=(10, 4)) ax = f.add_subplot(111) ax.set_title("PCA 1 Dimension") ax.scatter(AB_transformed_Reg, np.zeros_like(AB_transformed_Reg), color=colors)
- 1
- 2
- 3
- 4
- 5
- 6
- 7
- 8
- 9
- 10
- 11
- 12
- 13
- 14
- 15
- 16
- 17
- 18
- 19
- 20
- 21
- 22
- 23
- 24
- 25
- 26
- 27
- 28
- 29
- 30
- 31
- 32
- 33
- 34
- 35
- 36
- 37
- 38
- 39
- 40
- 41
- 42
构建的样本数据散点图如下:

KPCA处理后的结果如下:

PCA处理的结果如下:

从上述三张图片可以看出,针对非线性数据降维,KPCA的降维效果优于PCA方法
3.2 Case2:
样本数据散点图如下:

将样本数据升维又降维处理后的结果如下图:

具体实现代码
#构建样本数据 from sklearn.datasets import make_moons from scipy.spatial.distance import pdist, squareform X, y = make_moons(n_samples=200, random_state=123) plt.scatter(X[y==0, 0], X[y==0, 1], color='r', marker='^', alpha=.4) plt.scatter(X[y==1, 0], X[y==1, 1], color='b', marker='o', alpha=.4) #KPCA处理结果 def rbf_kpca(X, gamma, k): sq_dist = pdist(X, metric='sqeuclidean') # N = X.shape[0] # sq_dist.shape = N*(N-1)/2 mat_sq_dist = squareform(sq_dist) # mat_sq_dist.shape = (N, N) # step 1 K = np.exp(-gamma*mat_sq_dist) # step 2 N = X.shape[0] one_N = np.ones((N, N))/N K = K - one_N.dot(K) - K.dot(one_N) + one_N.dot(K).dot(one_N) # step 3 Lambda, Q = np.linalg.eig(K) eigen_pairs = [(Lambda[i], Q[:, i]) for i in range(len(Lambda))] eigen_pairs = sorted(eigen_pairs, reverse=True, key=lambda k: k[0]) return np.column_stack((eigen_pairs[i][1] for i in range(k))) #调用上述自定义函数 X_kpca = rbf_kpca(X, gamma=15, k=2) #将降维处理后的数据绘制出来 fig, ax = plt.subplots(1, 2, figsize=(8, 4)) ax[0].scatter(X_kpca[y==0, 0], X_kpca[y==0, 1], color='r', marker='^', alpha=.4) ax[0].scatter(X_kpca[y==1, 0], X_kpca[y==1, 1], color='b', marker='o', alpha=.4) label_count = np.bincount(y) # 统计各类别出现的次数 # label_count[0] = 500 # label_count[1] = 500 ax[1].scatter(X_kpca[y==0, 0], np.zeros(label_count[0]), color='r') ax[1].scatter(X_kpca[y==1, 0], np.zeros(label_count[1]), color='b') # y轴置零 # 投影到x轴 ax[1].set_ylim([-1, 1]) ax[0].set_xlabel('PC1') ax[0].set_ylabel('PC2') ax[1].set_xlabel('PC1') plt.show()
- 1
- 2
- 3
- 4
- 5
- 6
- 7
- 8
- 9
- 10
- 11
- 12
- 13
- 14
- 15
- 16
- 17
- 18
- 19
- 20
- 21
- 22
- 23
- 24
- 25
- 26
- 27
- 28
- 29
- 30
- 31
- 32
- 33
- 34
- 35
- 36
- 37
- 38
- 39
- 40
- 41
- 42
- 43
- 44
- 45
- 46
- 47
- 48
- 49
注:核函数处理非线性分离效果很好,但是一不小心就可能导致拟合过度。
参考文献:
1. http://blog.csdn.net/u013719780
2. https://blog.csdn.net/lanchunhui/article/details/50492482
声明:本文内容由网友自发贡献,不代表【wpsshop博客】立场,版权归原作者所有,本站不承担相应法律责任。如您发现有侵权的内容,请联系我们。转载请注明出处:https://www.wpsshop.cn/w/很楠不爱3/article/detail/129104
推荐阅读
相关标签



